SIDURI : un système d'information au service de l’innovation pilotée par les données dans la fermentation alimentaire
Emilie FERNANDEZ, Agnès BARNABE, Erwan LE FLOCH, Thomas LACROIX, Jonathan MINEAU-CESARI, Sophie SCHBATH et Valentin LOUX
Les consommateurs reconsidèrent leurs habitudes alimentaires et recherchent des aliments durables, résilients, sûrs et nutritifs. Les procédés de fermentation ont démontré au fil des années leur capacité à améliorer naturellement la bioconservation, les propriétés fonctionnelles et les caractéristiques sensorielles dans une grande diversité de matrices alimentaires. Le Grand Défi français « Ferments du Futur » (FdF), un partenariat public-privé de dix ans lancé en 2022, vise à stimuler l’innovation en fermentation grâce à une approche fondée sur les données pour la conception de nouveaux aliments fermentés. Chaque année, FdF finance des projets de recherche précompétitifs couvrant l’écologie microbienne, la caractérisation sensorielle et biochimique, la conception de bioprocédés et les interactions hôte–microorganismes. Un lot de travaux de FdF, piloté par la plateforme de bioinformatique Migale, est consacré au développement de Siduri, un portail web convivial conçu pour centraliser le volume important de données générées par ces projets. Le développement de Siduri est complété par un programme de gestion des données soutenant les projets FdF ainsi que par l’intégration de capacités standardisées d’analyse bioinformatique.
Le portail web Siduri offre une interface conviviale permettant aux chercheurs et aux partenaires industriels d’accéder aux jeux de données générés dans le cadre de FdF, de les explorer et de les gérer. La plateforme s’appuie sur l’architecture modulaire d’OpenSILEX \[1\], combinant un backend Java et un frontend Vue.js, et intègre plusieurs ontologies décrivant les ressources biologiques, les processus expérimentaux, les jeux de données et les analyses. Les développements récents portent notamment sur la gestion des ressources génétiques telles que les souches microbiennes, élément clé de la recherche en fermentation. Étant donné que FdF implique à la fois des acteurs académiques et industriels, le portail met en œuvre des politiques d’accès multiniveaux, allant de jeux de données privés à des données sous embargo accessibles uniquement au consortium. Les travaux en cours visent à affiner les mécanismes de contrôle d’accès afin de permettre la délégation des responsabilités de gestion des données aux responsables de projet tout en garantissant un partage sécurisé. La plateforme est hébergée sur l’infrastructure Migale et intègre diverses sources de données, notamment des données publiques, des données issues des projets FdF et des jeux de données fournis par des partenaires collaboratifs ou industriels.
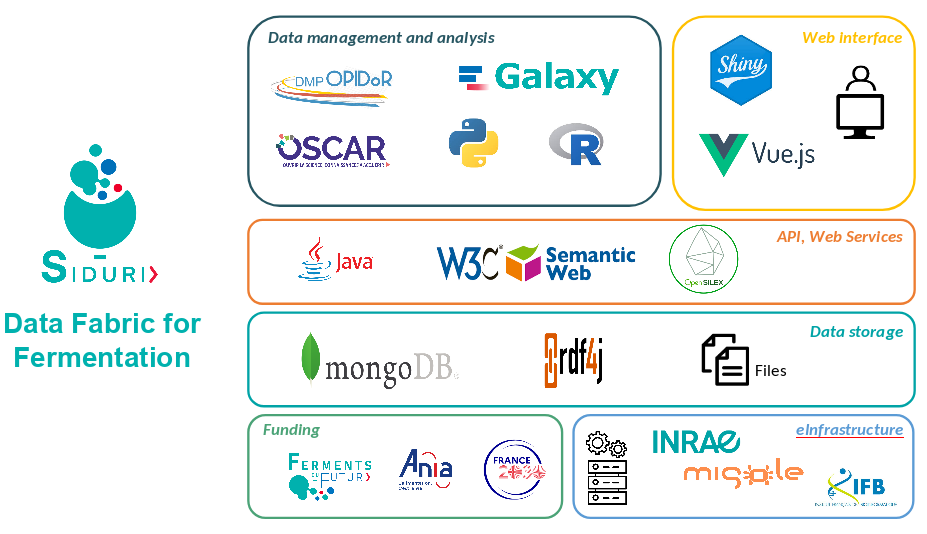
L’ambition du développement de Siduri, au-delà de son organisation de gestion des données et de son interface web, est de fournir des capacités d’analyse bioinformatique standardisées et à l’état de l’art. Ainsi, la création d’un catalogue d’outils et de workflows recommandés a été initiée à partir de métadonnées extraites du registre bio.tools \[2\] et de l’ontologie EDAM \[3\]. Les ressources sont dans un premier temps issues de la littérature et de communautés scientifiques existantes telles que microGalaxy \[4\]. En complément des ressources publiques, ce catalogue peut être enrichi par des scripts développés dans le cadre des projets FdF. L’équipe Siduri accompagne d’ailleurs les développeurs FdF dans la conception, le packaging et le partage de leurs outils via Galaxy, notamment par la création de wrappers et la structuration des workflows. Étant donné que FdF peut appliquer une politique stricte de confidentialité des données, une instance dédiée de Galaxy est déployée et hébergée sur l’infrastructure Migale afin de garantir un stockage et un accès sécurisés. Les outils et workflows identifiés dans le catalogue seront disponibles sur cette instance, permettant aux partenaires FdF de réaliser facilement des analyses bioinformatiques.
Siduri constitue une véritable « data fabric » combinant gouvernance et gestion des données, intégration sémantique, développement logiciel collaboratif et services de bioinformatique pour soutenir l’écosystème Ferments du Futur. Les développements futurs porteront sur l’extension du catalogue de workflows d’analyse, l’amélioration de l’interopérabilité et le renforcement des mécanismes de contrôle d’accès, tout en maintenant une gouvernance robuste des données pour la recherche collaborative impliquant partenaires académiques et industriels.
Ce travail a bénéficié d’une aide de l’État gérée par l’Agence Nationale de la Recherche (ANR) dans le cadre du programme France 2030, référence ANR-22-GDFF-0001.
References
1. Neveu P, et al. Dealing with multi-source and multi-scale information in plant phenomics: the ontology-driven Phenotyping Hybrid Information System. New Phytol. 2019;221(1):588–601.
2. Ison J, et al. The bio.tools registry of software tools and data resources for the life sciences. Genome Biol. 2019 Aug 12;20(1):164.
3. Ison J, et al. EDAM: an ontology of bioinformatics operations, types of data and identifiers, topics and formats. Bioinformatics. 2013 May 15;29(10):1325–32.
4 . Nasr E, et al. Microbiology Galaxy Lab: The first community-driven gateway for reproducible and FAIR analysis of microbial data. bioRxiv [Preprint]. 2025 Sep 16:2024.12.23.629682. doi: 10.1101/2024.12.23.629682. PMID: 39764050; PMCID: PMC11703195.